ARN ribossomal 16S
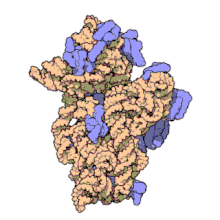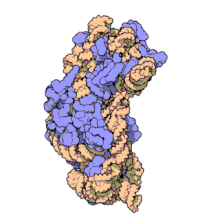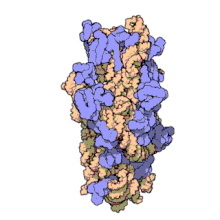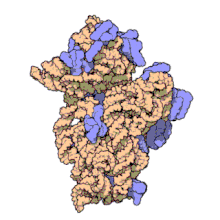
RNA ribossomal 16s (ou 16S rRNA) é um componente da pequena subunidade 30S dos ribossomos procarióticos. Devido as baixas taxas de evolução da região, o 16S rRNA é utilizado em reconstrução filogenética.[2][3]
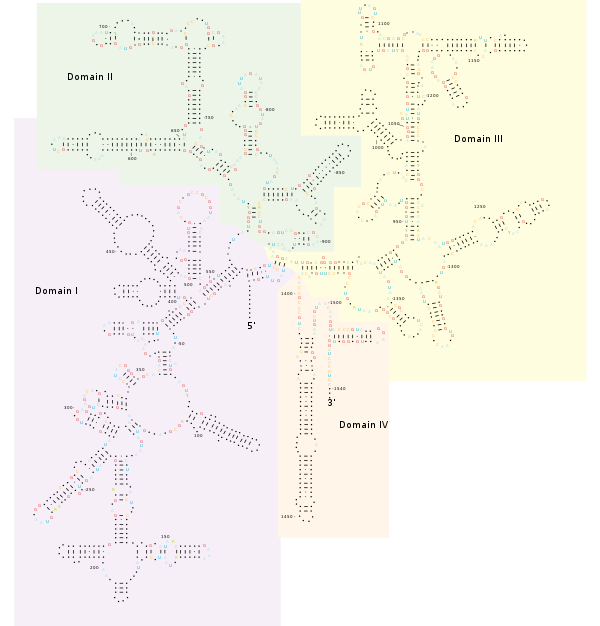
Múltiplas sequências de 16S rRNA em uma única bactéria.[4]
Os estudos que utilizam o 16 rRNA, se utilizam da sequência no DNA que codifica a região 16S e realiza comparações com outros procariontes, tendo em vista a baixa taxa de mutação nessa região do DNA. Até o ano de 2020 esse método é considerado de referência para análise da taxonomia de bactérias.[5]
O método se trata de encontrar a região 16S da bactéria e realizar seu isolamento por primers (fazem a seleção do local a ser amplificado) específicos, após essa etapa é realizada a Reação em cadeia das polimerases (PCR) com o objetivo de aumentar grandemente o número de cópias dessa região.[6] Após essa etapa as cópias são utilizados em uma máquina de sequenciamento genético, sendo o aumento no número de cópias essencial para detecção no sequenciador[7]
Estrutura[editar | editar código-fonte]
Referências
- ↑ Schluenzen F, Tocilj A, Zarivach R, Harms J, Gluehmann M, Janell D, Bashan A, Bartels H, Agmon I, Franceschi F, Yonath A Structure of functionally activated small ribosomal subunit at 3.3 angstroms resolution (2000). «Structure of functionally activated small ribosomal subunit at 3.3 angstroms resolution». Cell. 102 (5): 615–23. PMID 11007480. doi:10.1016/S0092-8674(00)00084-2
- ↑ Woese, Carl R.; George E. (1 de novembro de 1977). «Phylogenetic structure of the prokaryotic domain: The primary kingdoms». Proceedings of the National Academy of Sciences (em inglês). 74 (11): 5088-5090. ISSN 0027-8424. PMID 270744. doi:10.1073/pnas.74.11.5088
- ↑ Woese, Carl R.; Kandler, O; Wheelis, M (1990). «Towards a natural system of organisms: proposal for the domains Archaea, Bacteria, and Eucarya». Proc Natl Acad Sci USA. 87 (12): 4576–9. Bibcode:1990PNAS...87.4576W. PMC 54159
 . PMID 2112744. doi:10.1073/pnas.87.12.4576
. PMID 2112744. doi:10.1073/pnas.87.12.4576
- ↑ Case RJ, Boucher Y, Dahllöf I, Holmström C, Doolittle WF, Kjelleberg S (janeiro de 2007). «Use of 16S rRNA and rpoB Genes as Molecular Markers for Microbial Ecology Studies». Appl. Environ. Microbiol. 73 (1): 278–88. PMC 1797146
 . PMID 17071787. doi:10.1128/AEM.01177-06
. PMID 17071787. doi:10.1128/AEM.01177-06
- ↑ Lange, Carla C.; Brito, Maria A. V. P.; Brito, José R. F.; Arcuri, Edna F.; Souza, Guilherme N.; Machado, Marco A.; Domingues, Robert; Salimena, Alessandra P. S. (Janeiro de 2011). «Uso de PCR e sequenciamento do rDNA 16S para identificação de bactérias do gênero Staphylococcus isoladas de mastite bovina». Pesquisa Veterinária Brasileira. 31 (1): 36–40. ISSN 0100-736X. doi:10.1590/S0100-736X2011000100006
- ↑ Adzitey, Frederick; Huda, Nurul; Ali, Gulam Rusul Rahmat (1 de abril de 2013). «Molecular techniques for detecting and typing of bacteria, advantages and application to foodborne pathogens isolated from ducks». 3 Biotech (em inglês). 3 (2): 97–107. ISSN 2190-5738. PMC 3597138
 . PMID 28324565. doi:10.1007/s13205-012-0074-4
. PMID 28324565. doi:10.1007/s13205-012-0074-4
- ↑ Mardis, Elaine R. (Setembro de 2008). «Next-Generation DNA Sequencing Methods». Annual Review of Genomics and Human Genetics (em inglês). 9 (1): 387–402. ISSN 1527-8204. doi:10.1146/annurev.genom.9.081307.164359
