Z-DNA

O Z-DNA, DNA-Z, ADN-Z ou Z-ADN é uma das conformações que a estrutura de DNA pode assumir e foi descrito pela primeira vez em 1970.[1] Ao contrário da forma B-DNA, mais comumente encontrada, o Z-DNA tem a sua torção para a esquerda a cada 12 pares de base com 18 Å de diâmetro. De um modo geral, o DNA assume essa conformação em segmentos com sequências de bases de purina-pirimidina alternadas. O Z-DNA é estabilizado em altas concentrações de sal, devido a redução das repulsões eletrostáticas entre os grupos fosfato mais próximos nas cadeias opostas (8 Å no Z-DNA versus 12 Å no B-DNA).[2] As funções biológicas do Z-DNA ainda são pouco conhecidas. Acredita-se que durante a transcrição, o Z-DNA possa aliviar a tensão gerada pela torção do DNA, está associado a super enrolamento negativo.[3] Além disso, alguns carcinógenos podem modificar os nucleotídeos formando adutos que induzem a formação do Z-DNA, o que sugere que essa conformação pode ter um papel importante no câncer.[4][5]
História e estudo
[editar | editar código-fonte]O DNA canhoto foi descoberto por Robert Wells e seus colegas ao estudar um polímero formado por repetições de inosina-citosina.[6] Eles observaram um dicroísmo circular "reverso" em tal DNA, do qual eles chegaram à conclusão correta de que suas hélices se torcem na direção da esquerda. Posteriormente, foi publicada a estrutura cristalina do Z-DNA, onde a análise de difração de raios-X revelou que este é o primeiro fragmento de DNA de cristal único (hexâmero de DNA auto-complementar d(CG)3). Descobriu-se que o Z-DNA é uma hélice dupla do DNA de duas cadeias anti-paralelas conectadas por ligações entre pares de bases nitrogenadas . Estas obras foram realizadas por Andrew Wang, Alexander Rich e sua equipe no Massachusetts Institute of Technology (Instituto de Tecnologia de Massachusetts).[7]
Em 1970, foi demonstrado que o DNA mais comum da forma B pode se tornar na forma Z. Neste experimento, foi demonstrado que o dicroísmo circular do polímero (dG-dC) em raios ultravioleta com uma solução de 4M de NaCl mudou para o exato oposto.[8] O fato de que durante essa transição a forma B passada para a forma Z foi confirmada pelos resultados da espectroscopia Raman.[9] A cristalização dos Compostos B e Z-DNA, realizada em 2005,[10] deu uma melhor compreensão do papel potencial que o Z-DNA desempenha na célula. Onde quer que haja segmentos de formas de Z-DNA, também deve haver compostos B-Z em suas extremidades conectando a forma Z com a forma B encontrada em todo o restante do genoma.
Em 2007, a versão RNA do Z-DNA, o Z-RNA, foi descrito como uma forma alternativa do A-RNA em uma hélice canhota.[11] A transição do A-RNA para o Z-RNA, no entanto, já foi descrita em 1984.[12]
Estrutura
[editar | editar código-fonte]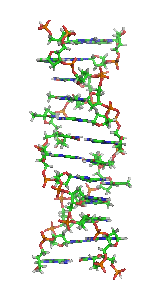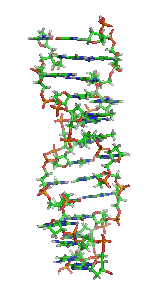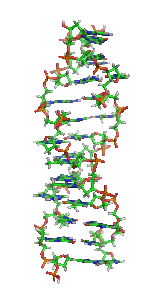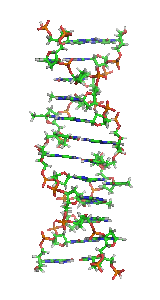
O Z-DNA é significativamente diferente das formas destras. O Z-DNA é canhoto e tem uma estrutura primária, repetida a cada 2 pares de bases. Existem 12 pares de bases por turno da hélice. Em contraste com o A-DNA e o B-DNA, no Z-DNA o sulco principal é pouco distinguível, o sulco menor é estreito e profundo.[13] Em geral, a estrutura do Z-DNA é energeticamente desfavorável, embora algumas condições possam ativar sua formação, tais como: sequências alternadas de purina-pirimidina (especialmente poli(dGC)2), superenrolamento negativo de DNA, alto teor de sal e alguns cátions (todos na temperatura fisiológica de 37ºC e pH 7,3 a 7,4). O Z-DNA pode se ligar ao B-DNA em uma estrutura, levando ao deslocamento dos pares de bases (veja a figura "Endoconformação C2' e C3' de açúcares").[14]

Outra característica do Z-DNA é a alternância de conformações de resíduos de nucleotídeos. A desoxicitidina está em uma conformação padrão: açúcar na endoconformação C2' (veja a figura do lado esquerdo), e a base está em anti-conformação (isto é, a base é girada na direção oposta ao grupo hidroxila no quinto átomo de carbono; nesta posição estão as bases na cadeia polinucleotídica[15]). Em desoxiguanosina açúcar está em endoconformação C3', e tem uma base extremamente atípica syn-conformação.[16]
O empilhamento de bases no Z-DNA tem novas propriedades inerentes apenas a esta forma. Assim, interações de empilhamento existem apenas entre os resíduos de citosina de cadeias opostas e os resíduos de guanina não interagem entre si.[17]
Fosfatos no Z-DNA não são equivalentes entre si e são removidos a várias distâncias do eixo da hélice; para nucleotídeos de guanina, essa distância é de 0,62 nm e para nucleotídeos de citosina - 0,76 nm. Ao mesmo tempo, os açúcares vizinhos “olham” em direções opostas e, por causa disso, a linha que conecta sequencialmente átomos de fósforo em uma cadeia torna-se um ziguezague (daí o nome Z-DNA).[17]

A estrutura do Z-DNA é difícil de estudar, porque praticamente não existe na forma estável de uma dupla hélice. Em contraste, a hélice Z-DNA canhota é uma estrutura temporária que aparece como resultado da atividade biológica e desaparece rapidamente.[18]
Transição do B-DNA para o Z-DNA
[editar | editar código-fonte]Como já mencionado, as formas B e Z são capazes de entrar umas nas outras. Isso acontece quando a força iônica da solução ou a concentração de cátions que neutralizam a carga negativa da estrutura do fosfodiéster muda. Assim, para a transição não é necessário para o circuito de divergência, que é iniciada quebrando as ligações de hidrogênio por vários pares de bases seguido de uma guanina fixo syn-conformação, ligações de hidrogênio são restauradas e forma anti-base de pares de Watson-Crick. A região de transição se move em espiral na forma de um loop ou laço.[17]
Prever a estrutura do Z-DNA
[editar | editar código-fonte]Atualmente é possível prever uma sequência de DNA plausível na forma de Z-DNA. Um algoritmo para prever a propensão do DNA a se reorganizar da forma B para a forma Z, ZHunt, foi escrito em 1984 pelo Dr. P. Shing Ho, do Instituto de Tecnologia de Massachusetts.[19] Mais tarde, este algoritmo foi desenvolvido por Tracy Camp e colegas para determinar a formação do Z-DNA em todo o genoma.[20]
O algoritmo ZHunt está disponível em Z-Hunt online.
Importância biológica
[editar | editar código-fonte]O DNA-Z foi encontrado em representantes de todos os três domínios da vida: archaea (particularmente em haloarreus[21]), bactérias e eucariotos.[13] Até agora, nenhuma função biológica clara do Z-DNA foi identificada, no entanto, acredita-se que esteja envolvida na regulação da expressão gênica no nível da transcrição. De fato, é confiável que uma sequência de dm5-dG está associada à regulação da expressão gênica em eucariotos, que está em condições fisiológicas na forma de Z-DNA. Esta regulação pode ser mediada por um superenrolamento, uma ligação ou uma proteína específica para o Z-DNA, identificado por cátions do tipo espermidina e metilação da desoxicitidina.[22]
A suposição de que o Z-DNA fornece o superenrolamento do DNA durante a transcrição[10] é apoiada pelo fato de que o potencial para a formação de formas Z é encontrado nos locais envolvidos na transcrição ativa. Foi mostrada uma ligação entre os locais de formação do Z-DNA nos genes do 22º cromossoma humano e os locais conhecidos para o início da transcrição.[20]
O Z-DNA é formado após o início da transcrição. O primeiro domínio, que se liga ao Z-DNA e tem alta afinidade por ele , foi encontrado na enzima ADA (adenosina deaminase específica do RNA)[23][24] (este domínio é chamado de domínio Z-alpha). Estudos de ressonância magnética nuclear de proteínas confirmaram que este domínio se liga ao Z-DNA, independentemente de sua sequência nucleotídica.[25][26][27] Em fontes semelhantes foram encontrados em várias outras proteínas homólogas ao ADA.[24] A identificação do domínio Z-alfa formou a base para a caracterização do Z-RNA e do composto B com o Z-DNA. Estudos mostraram que o domínio ADA que liga o Z-DNA permite que esta enzima seja localizada nos locais de transcrição ativa, onde desempenha sua função (altera a sequência do RNA recém-formado).[28][29]
Em 2003, o biofísico Alexander Rich, do Instituto de Tecnologia de Massachusetts, observou que o fator de virulência de um poxvírus, chamado Vaccinia (VACV), tem uma relação ao Z-alfa que é semelhante à ligação de Z-DNA de mamíferos.[30][31] Em 2005, Rich e seus colegas descobriram qual o valor do VACV para o poxvírus. Quando a expressão dos genes VACV causa um aumento de 5 a 10 vezes na transcrição de vários genes da célula hospedeira, esses genes bloqueiam a capacidade das células de se autodestruírem (apoptose) como uma reação protetora contra a infecção.
Rich sugeriu que o DNA-Z é necessário para a transcrição e o VACV estabiliza o Z-DNA, aumentando assim a expressão de genes anti-apoptóticos. Ele também apresentou a ideia de que moléculas pequenas podem se ligar ao VACV, impedindo a proteína de se combinar com o Z-DNA e, por fim, interferir na expressão de genes anti-apoptóticos. Isso pode potencialmente ser usado como base para a proteção contra a varíola causada por poxvírus.
Usando anticorpos para o Z-DNA, esta forma de DNA foi encontrada nas regiões interdígidas dos cromossomos politênicos. O fato é que os nucleossomos estão apenas no B-DNA, e a transição para a forma Z destrói a estrutura do nucleossomo e, portanto, consiste em nucleossomas da cromatina. A este respeito, assume-se que a forma Z pode desempenhar um papel regulador, especialmente porque a transição B → Z é reversível.[17]
Foi estabelecido que o efeito tóxico do brometo de etídio nos tripanossomas está associado à transição do DNA do cinetoplasto para a forma Z. Este efeito é devido à intercalação de EtBr em DNA, devido a que o DNA perde sua estrutura nativa, se dispersa, adquirindo a forma de Z e, por causa disso, torna-se incapaz de replicação.[32]
Comparação de parâmetros geométricos de algumas formas de DNA
[editar | editar código-fonte]
| Parâmetro | Forma A | Forma B | Forma Z |
|---|---|---|---|
| Direção | direita | direita | esquerda |
| Repetição da torção
(em pares de bases) |
1 par de bases | 1 par de bases | 2 pares de bases |
| Rotatividade (em graus) | 32,7º | 34,3º | 30º |
| Pares de bases por turno | 11 | 10,5 | 12 |
| Inclinação dos pares de bases | +19º | -1,2º | -9º |
| Subida ao longo da hélice
(em pares de bases) |
2,3 Å (0,23 nm) | 3,32 Å (0,332 nm) | 3,8 Å (0,38 nm) |
| Uma volta da hélice | 28,2 Å
(2,82 nm) |
33,2 Å
(3,32 nm) |
45,6 Å
(4,56 nm) |
| Torção média da hélice | +18º | +16º | 0º |
| Ângulo do glicosil | anti | anti | C: anti
G: syn |
| Conformação de açúcar | C3'-endo | C2'-endo | C: C2'-endo
G: C3'-endo |
| Diãmetro | 23 Å (2,3 nm) | 20 Å (2,0 nm) | 18 Å (1,8 nm) |
Ver também
[editar | editar código-fonte]- A-DNA
- B-DNA
- DNA
- DNA superenrolado
- Vaccinia (VACV)
Ligações externas
[editar | editar código-fonte]- «Z-Hunt online». (em inglês).
Referências
- ↑ MITSUI, Y.; LANGRIDGE, R.; SHORTLE, BARBARA E.; CANTOR, CHARLES R.; GRANT, ROBERT C.; KODAMA, MASAHIKO; WELLS, ROBERT D. (Dezembro de 1970). «Physical and Enzymatic Studies on Poly d(I–C).Poly d(I–C), an Unusual Double-helical DNA». Nature (em inglês). 228 (5277): 1166–1169. ISSN 0028-0836. doi:10.1038/2281166a0
- ↑ Donald,, Voet, (2011). Biochemistry 4th edition ed. Hoboken, NJ: John Wiley & Sons. ISBN 9780470570951. OCLC 690489261
- ↑ Rich, Alexander; Zhang, Shuguang (Julho de 2003). «Timeline: Z-DNA: the long road to biological function». Nature Reviews. Genetics. 4 (7): 566–572. ISSN 1471-0056. PMID 12838348. doi:10.1038/nrg1115
- ↑ Vongsutilers, V.; Gannett, P. M. (2018). «C8-Guanine modifications: effect on Z-DNA formation and its role in cancer». Organic & Biomolecular Chemistry (em inglês). 16 (13): 2198–2209. ISSN 1477-0520. doi:10.1039/c8ob00030a
- ↑ Zhao, Junhua; Bacolla, Albino; Wang, Guliang; Vasquez, Karen M. (1 de setembro de 2009). «Non-B DNA structure-induced genetic instability and evolution». Cellular and Molecular Life Sciences (em inglês). 67 (1): 43–62. ISSN 1420-682X. PMC 3017512
 . PMID 19727556. doi:10.1007/s00018-009-0131-2
. PMID 19727556. doi:10.1007/s00018-009-0131-2
- ↑ Mitsui et al. (1970). «Physical and enzymatic studies on poly d(I-C)-poly d(I-C), an unusual double-helical DNA». Nature (London) 228 (5277): 1166–1169.
- ↑ Wang, Andrew H.-J.; Quigley, Gary J.; Kolpak, Francis J.; Crawford, James L.; van Boom, Jacques H.; van der Marel, Gijs; Rich, Alexander (Dezembro de 1979). «Molecular structure of a left-handed double helical DNA fragment at atomic resolution». Nature (em inglês). 282 (5740): 680–686. ISSN 0028-0836. doi:10.1038/282680a0
- ↑ «Salt-induced co-operative conformational change of a synthetic DNA: Equilibrium and kinetic studies with poly(dG-dC)». Journal of Molecular Biology (em inglês). 67 (3): 375–396. 28 de junho de 1972. ISSN 0022-2836. doi:10.1016/0022-2836(72)90457-3
- ↑ Thamann, Thomas J.; Lord, Richard C.; Wang, Andrew H.J.; Rich, Alexander (1981). «The high salt form of poly(dG-dC)·poly(dG-dC) is left-handed Z-DNA: Raman spectra of crystals and solutions». Nucleic Acids Research (em inglês). 9 (20): 5443–5458. ISSN 0305-1048. doi:10.1093/nar/9.20.5443
- ↑ a b Ha, Sung Chul; Lowenhaupt, Ky; Rich, Alexander; Kim, Yang-Gyun; Kim, Kyeong Kyu (Outubro de 2005). «Crystal structure of a junction between B-DNA and Z-DNA reveals two extruded bases». Nature (em inglês). 437 (7062): 1183–1186. ISSN 0028-0836. doi:10.1038/nature04088
- ↑ Placido, Diana; Brown, Bernard A.; Lowenhaupt, Ky; Rich, Alexander; Athanasiadis, Alekos (Abril de 2007). «A Left-Handed RNA Double Helix Bound by the Zα Domain of the RNA-Editing Enzyme ADAR1». Structure (em inglês). 15 (4): 395–404. ISSN 0969-2126. doi:10.1016/j.str.2007.03.001
- ↑ Hall, Kathleen; Cruz, Phillip; Tinoco, Ignacio; Jovin, Thomas M.; van de Sande, Johan H. (Outubro de 1984). «'Z-RNA'—a left-handed RNA double helix». Nature (em inglês). 311 (5986): 584–586. ISSN 0028-0836. doi:10.1038/311584a0
- ↑ a b Nelson, Cox, David L., Michael M. Lehninger (2008). Principles of biochemistry. Nova York: W. H. Freeman and company. 1158 páginas. ISBN 978-0-7167-7108-1
- ↑ de Rosa, M.; de Sanctis, D.; Rosario, A. L.; Archer, M.; Rich, A.; Athanasiadis, A.; Carrondo, M. A. (3 de maio de 2010). «Crystal structure of a junction between two Z-DNA helices». Proceedings of the National Academy of Sciences (em inglês). 107 (20): 9088–9092. ISSN 0027-8424. doi:10.1073/pnas.1003182107
- ↑ Konichev A.S., Sevastyanova G. A. Molekularnaya biologiya (Молекулярная биология). — Editora: Akademiya (Академия), 2012. — 400 p. 82 — ISBN 978-5-7695-9147-1.
- ↑ Konichev A.S., Sevastyanova G. A. Molekularnaya biologiya (Молекулярная биология). — Editora: Akademiya (Академия), 2012. — 400 p. 92 — ISBN 978-5-7695-9147-1.
- ↑ a b c d Konichev A.S., Sevastyanova G. A. Molekularnaya biologiya (Молекулярная биология). — Editora: Akademiya (Академия), 2012. — 400 p. 93 — ISBN 978-5-7695-9147-1.
- ↑ Zhang, Haiyuan; Yu, Haijia; Ren, Jinsong; Qu, Xiaogang (Maio de 2006). «Reversible B/Z-DNA Transition under the Low Salt Condition and Non-B-Form PolydApolydT Selectivity by a Cubane-Like Europium-L-Aspartic Acid Complex». Biophysical Journal (em inglês). 90 (9): 3203–3207. ISSN 0006-3495. doi:10.1529/biophysj.105.078402
- ↑ Ho, P. S.; Ellison, M. J.; Quigley, G. J.; Rich, A. (Outubro de 1986). «A computer aided thermodynamic approach for predicting the formation of Z-DNA in naturally occurring sequences». The EMBO journal. 5 (10): 2737–2744. ISSN 0261-4189. PMC 1167176
 . PMID 3780676
. PMID 3780676
- ↑ a b Champ, P. Christoph; Maurice, Sandor; Vargason, Jeffrey M.; Camp, Tracy; Ho, P. Shing (2004). «Distributions of Z-DNA and nuclear factor I in human chromosome 22: a model for coupled transcriptional regulation». Nucleic Acids Research (em inglês). 32 (22): 6501–6510. ISSN 1362-4962. doi:10.1093/nar/gkh988
- ↑ Paul Blum. Archaea: Ancient Microbes, Extreme Environments, and the Origin of Life. — Academic Press, 2001. — Vol. 50. — p. 206. — (Advances in Applied Microbiology).
- ↑ Konichev A.S., Sevastyanova G. A. Molekularnaya biologiya (Молекулярная биология). — Editora: Akademiya (Академия), 2012. — 400 p. 93-94 — ISBN 978-5-7695-9147-1.
- ↑ Herbert, Alan G.; Rich, Alexander (1993). «A method to identify and characterize Z-DNA binding proteins using a linear oligodeoxynucleotide». Nucleic Acids Research (em inglês). 21 (11): 2669–2672. ISSN 0305-1048. doi:10.1093/nar/21.11.2669
- ↑ a b Herbert, A.; Alfken, J.; Kim, Y.-G.; Mian, I. S.; Nishikura, K.; Rich, A. (5 de agosto de 1997). «A Z-DNA binding domain present in the human editing enzyme, double-stranded RNA adenosine deaminase». Proceedings of the National Academy of Sciences (em inglês). 94 (16): 8421–8426. ISSN 0027-8424. doi:10.1073/pnas.94.16.8421
- ↑ Herbert, A (1 de agosto de 1998). «The Zalpha domain from human ADAR1 binds to the Z-DNA conformer of many different sequences». Nucleic Acids Research (em inglês). 26 (15): 3486–3493. ISSN 1362-4962. doi:10.1093/nar/26.15.3486
- ↑ Schwartz, Thomas; Rould, Mark A.; Lowenhaupt, Ky; Herbert, Alan; Rich, Alexander (11 de junho de 1999). «Crystal Structure of the Zα Domain of the Human Editing Enzyme ADAR1 Bound to Left-Handed Z-DNA». Science (em inglês). 284 (5421): 1841–1845. ISSN 0036-8075. PMID 10364558. doi:10.1126/science.284.5421.1841
- ↑ Schade, M.; Turner, C. J.; Kuhne, R.; Schmieder, P.; Lowenhaupt, K.; Herbert, A.; Rich, A.; Oschkinat, H. (26 de outubro de 1999). «The solution structure of the Zalpha domain of the human RNA editing enzyme ADAR1 reveals a prepositioned binding surface for Z-DNA». Proceedings of the National Academy of Sciences (em inglês). 96 (22): 12465–12470. ISSN 0027-8424. doi:10.1073/pnas.96.22.12465
- ↑ Herbert, A.; Rich, A. (9 de outubro de 2001). «The role of binding domains for dsRNA and Z-DNA in the in vivo editing of minimal substrates by ADAR1». Proceedings of the National Academy of Sciences (em inglês). 98 (21): 12132–12137. ISSN 0027-8424. doi:10.1073/pnas.211419898
- ↑ «Scientists observe biological activities of 'left-handed' DNA». MIT News
- ↑ Kim, Y.-G.; Muralinath, M.; Brandt, T.; Pearcy, M.; Hauns, K.; Lowenhaupt, K.; Jacobs, B. L.; Rich, A. (30 de maio de 2003). «A role for Z-DNA binding in vaccinia virus pathogenesis». Proceedings of the National Academy of Sciences (em inglês). 100 (12): 6974–6979. ISSN 0027-8424. doi:10.1073/pnas.0431131100
- ↑ Kim, Y.-G.; Lowenhaupt, K.; Oh, D.-B.; Kim, K. K.; Rich, A. (2 de fevereiro de 2004). «Evidence that vaccinia virulence factor E3L binds to Z-DNA in vivo: Implications for development of a therapy for poxvirus infection». Proceedings of the National Academy of Sciences (em inglês). 101 (6): 1514–1518. ISSN 0027-8424. doi:10.1073/pnas.0308260100
- ↑ Roy Chowdhury, Arnab; Bakshi, Rahul; Wang, Jianyang; Yildirir, Gokben; Liu, Beiyu; Pappas-Brown, Valeria; Tolun, Gökhan; Griffith, Jack D.; Shapiro, Theresa A. (16 de dezembro de 2010). «The Killing of African Trypanosomes by Ethidium Bromide». PLoS Pathogens (em inglês). 6 (12): e1001226. ISSN 1553-7374. PMC 3002999
 . PMID 21187912. doi:10.1371/journal.ppat.1001226
. PMID 21187912. doi:10.1371/journal.ppat.1001226
